低DNA用量、无扩增的PacBio建库技术助力基因组研究
 找药助理
找药助理
关键词: #健康资讯
 找药助理
找药助理
关键词: #健康资讯
基因组信息在生命科学研究中具有重要价值,尤其是在基因组学研究中,三代长读长测序组装技术的应用日益广泛。PacBio高保真测序技术以其高精度被视为三代测序的金标准。然而,PacBio标准建库方法对DNA输入量的要求较高,限制了其在小型昆虫或珍稀样本中的应用。虽然DNA扩增可以减少样本输入量,但容易引入扩增偏好和人工嵌合序列等错误,从而影响基因组的完整性及变异检测的准确性。因此,开发一种低DNA用量、无扩增且操作简便的PacBio建库方法显得尤为重要。
2024年7月5日,中国科学院动物研究所张勇研究组与中国农业科学院深圳农业基因组研究所阮珏研究组在《自然-通讯》(Nature Communications)上发表了一篇题为《Low-input PacBio sequencing generates high-quality individual fly genomes and characterizes mutational processes》的研究论文。该研究开发了一种基于Tn5转座酶的低DNA用量、无扩增、低成本的PacBio建库技术——LILAP。研究团队利用这一技术成功实现了两个单只雄性黑腹果蝇的全基因组测序和高质量组装,获得了内共生菌Wolbachia的完整基因组。基因组分析发现了两种突变特性:复杂转座事件更倾向于发生在non-B DNA序列富集区域,以及基因转换事件使转座子同质化。
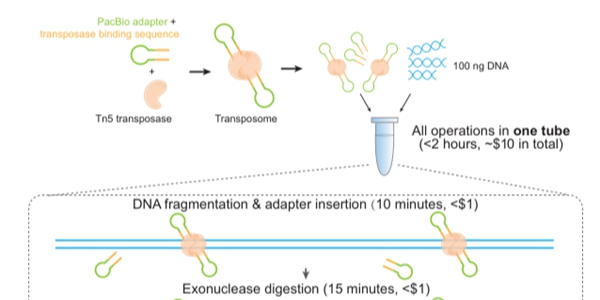
LILAP技术通过Tn5转座酶和发卡结构的PacBio测序接头组成二聚体转座复合物,一步实现DNA片段化和测序接头连接。整个流程在单个试管内进行,最大限度地减少了建库过程中DNA的损失,并简化了建库流程。此外,测序接头内可以添加条形码,用于多样本混合建库测序。
为了评估该技术,研究团队使用黑腹果蝇ISO1品系进行了测试。结果显示,两个单只果蝇的读段测序质量中位数达到了36,即碱基错误率低于0.02%。从头组装的基因组N50值超过6MB,质量分数超过60,即碱基错误率低于10^-6,保守单拷贝基因组装覆盖度大于98%,这些指标均超过了已发表的单只果蝇基因组质量。
此外,科研人员在全基因组组装结果中还发现了内共生微生物Wolbachia pipientis的完整基因组。通过检测Wolbachia基因组内的变异情况,他们发现了三个新突变,这为后续研究共生菌和宿主的互作提供了新的线索。
LILAP作为一种低DNA输入量的三代测序建库方法,在无需扩增的情况下将PacBio测序的DNA投入量降低至100ng,适用于解析小型生物及其内共生体基因组。未来,LILAP有望在小型生物多样性研究及较大物种的体细胞变异分析中得到广泛应用。例如,果蝇个体水平的全基因组关联分析、宿主-共生体协同进化研究等,都有望从这一技术中受益。
通过这一研究,LILAP展示了其在降低DNA用量需求、提高基因组测序质量方面的优势,为基因组学研究开辟了新的途径。这项技术不仅能推动对小型昆虫及珍稀样本的研究,还能为更大物种的基因组研究提供有力支持。LILAP的应用前景广阔,将进一步促进基因组学领域的研究和发展。

2025-12-14

2025-12-14

2025-12-14

2025-12-14

2025-12-14